Uso de la secuenciación de segunda generación (NGS) para descubrir la diversidad de hongos degradadores de la madera en los bosques Andino Patagónicos
Hongos degradadores de la madera en los bosques Andino Patagónicos
DOI:
Palabras clave:
Decaimiento, Hymenochaetales, Illumina, Nothofagus, PolyporalesResumen
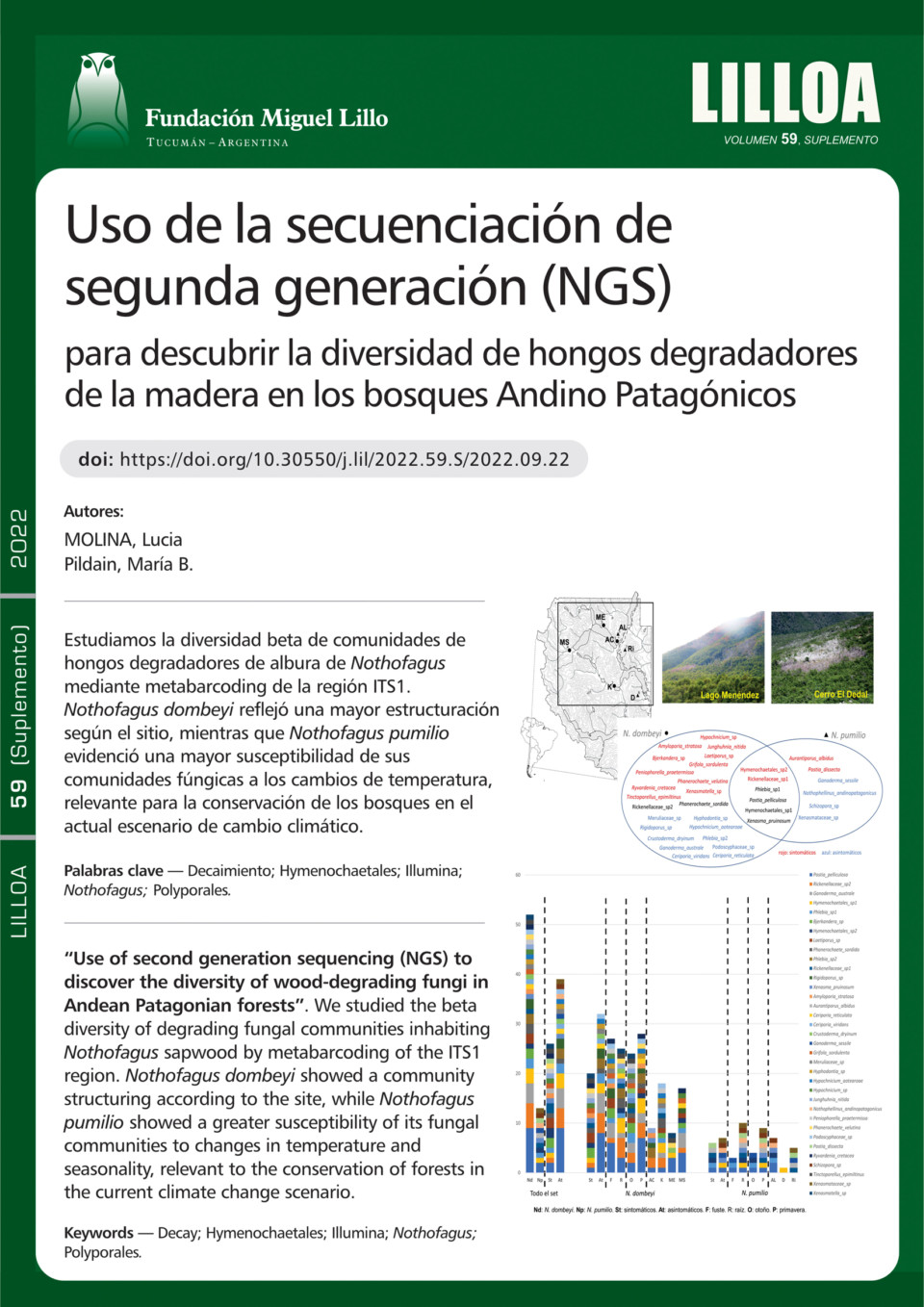
Los hongos son los principales degradadores de la madera en los ecosistemas boscosos, contribuyendo significativamente al ciclo global del carbono. Los enfoques metagenómicos basados en un amplicón específico (metabarcoding) constituyen una herramienta poderosa para su prospección y estudio. El objetivo principal de este estudio fue caracterizar a través de secuenciación de segunda generación (NGS), comunidades de hongos degradadores en la albura de dos especies de Nothofagus de los bosques del norte de la Patagonia, para evaluar patrones de diversidad en sitios, estaciones, hospedadores, compartimentos del árbol y condiciones de salud, como una contribución a la autoecología de las especies de este género. Nuestro estudio comprendió tres pasos metodológicos principales: (i) muestreo de madera de árboles vivos sanos y enfermos de las especies forestales N. dombeyii y N. pumilio; (ii) extracción de ADN, amplificación y secuenciación de la región ITS1 en la plataforma MiSeq Illumina, (iii) procesamiento de lecturas y extracción de datos de los órdenes Polyporales e Hymenochaetales y (iv) análisis de datos e interpretación. Se obtuvieron un total de 35 unidades taxonómicas (variantes de secuencia de amplicón -ASV-), las cuales fueron asignadas a 23 géneros de hongos putativos en 15 familias. Postia pelliculosa fue la especie detectada con mayor frecuencia en el estudio. El hospedador fue el factor más fuerte entre las variables estudiadas en cuanto a su efecto sobre la estructura y la composición de la comunidad fúngica analizada. Para N. dombeyi, que se distribuye en una amplia gama de condiciones climáticas, el sitio fue el modelador más fuerte de sus comunidades, mientras que para N. pumilio se observó una mayor susceptibilidad a los cambios de temperatura y estacionalidad, que son, ciertamente, factores relevantes para la conservación de los bosques en el actual escenario de cambio climático. Este es el primer estudio que utiliza NGS como una estrategia rápida y a gran escala para descubrir la diversidad de hongos que degradan la madera en los bosques templados de Patagonia.
Descargas
Citas
Altschul, S., Madden, T. L., Schäffer, A. A., Zhang, J., Zhang, Z., Miller, W. y Lipman, D. J. (1997). Gapped BLAST and PSI-BLAST: a new generation of protein database search programs. Nucleic Acids Research 25 (17): 3389-3402. https://doi.org/10.1093/nar/25.17.3389
Anderson, M. J. (2017). Permutational Multivariate Analysis of Variance (PERMANOVA ). En Wiley StatsRef: Statistics Reference Online (pp. 1–15). Wiley. https://doi.org/10.1002/9781118445112.stat07841
Anslan, S., Nilsson, R. H., Wurzbacher, C., Baldrian, P., Tedersoo, L. y Bahram, M. (2018). Great differences in performance and outcome of high-throughput sequencing data analysis platforms for fungal metabarcoding. MycoKeys 39: 29-40. https://doi.org/10.3897/mycokeys.39.28109
Arantes, V, y Goodell, B. (2014). Current understanding of brownrot fungal biodegradation mechanisms: a review. In: Deterioration and protection of sustainable biomaterials. ACS Publications; p. 3–21.
Bahram, M., Küngas, K., Pent, M., Põlme, S., Gohar, D. y Põldmaa, K. (2022). Vertical stratification of microbial communities in woody plants. Phytobiomes Journal 6 (2): 161-168 . https://apsjournals.apsnet.org/doi/10.1094/PBIOMES-06-21-0038-R
Baldrian, P. (2016). Forest microbiome: diversity, complexity and dynamics. FEMS Microbiology Reviews 41 (2): 109-130. https://doi.org/10.1093/femsre/fuw040
Barroetaveña, C., Salomón, M. E. S. y Bassani, V. (2019). Rescuing the ectomycorrhizal biodiversity associated with South American Nothofagaceae forest, from the 19th century naturalists up to molecular biogeography. Forestry: An International Journal of Forest Research 92 (5): 500-511. https://doi.org/10.1093/forestry/cpz047
Baselga, A., Orme, D., Villéger, S., De Bortoli, J., Leprieur, F. y Logez, M. (2022). Partitioning beta diversity into turnover and nestedness components. En R package version 1.5.6. https://cran.r-project.org/package=betapart
Blanchette, R. A. (1991). Delignification by Wood-Decay Fungi. Annual Review of Phytopathology 29 (1): 381-403. https://doi.org/10.1146/annurev.py.29.090191.002121
Brown, S. P., Veach, A. M., Rigdon-Huss, A. R., Grond, K., Lickteig, S. K., Lothamer, K., Oliver, A. K. y Jumpponen, A. (2015). Scraping the bottom of the barrel: are rare high throughput sequences artifacts? Fungal Ecology 13: 21-225. https://doi.org/10.1016/j.funeco.2014.08.006
Buchanan, P. K. y Hood, I. A. (1992). New species and new records of Aphyllophorales (Basidiomycetes) from New Zealand. New Zealand Journal of Botany 30 (1): 95-112. https://doi.org/10.1080/0028825X.1992.10412888
Callahan, B. J., McMurdie, P. J., Rosen, M. J., Han, A. W., Johnson, A. J. A. y Holmes, S. P. (2016). DADA2: High-resolution sample inference from Illumina amplicon data. Nature Methods 13 (7): 581-583. https://doi.org/10.1038/nmeth.3869
Goodell, B., Winandy, J. E. y Morrell, J. J. (2020). Fungal Degradation of Wood: Emerging Data, New Insights and Changing Perceptions Coatings 10 (12): 1210. https://doi.org/10.3390/coatings10121210
Cunningham, G. H. (1965). Polyporaceae of New Zealand. En D. of S. y I. Research (Ed.), Transactions. https://doi.org/10.2307/3756787
Dai, Y.-C. (2005). Illustrations of Pathogenic Wood-Decaying Fungi in China. Science Press.
Daniels, L. D. y Veblen, T. T. (2004). Spatiotemporal influences of climate on altitudinal treeline in northern Patagonia. Ecology 85 (5): 1284-1296. https://doi.org/10.1890/03-0092
de Errasti, A., de Beer, Z. W., Coetzee, M. P. A., Roux, J., Rajchenberg, M. y Wingfield, M. J. (2016). Three new species of Ophiostomatales from Nothofagus in Patagonia. Mycological Progress 15 (2): 1-17. https://doi.org/10.1007/s11557-016-1158-z
de Errasti, A., de Beer, Z. W., Rajchenberg, M., Coetzee, M. P. A., Wingfield, M. J. y Roux, J. (2015). Huntiella decorticans sp. nov. (Ceratocystidaceae) associated with dying Nothofagus in Patagonia. Mycologia 107 (3): 512-521. https://doi.org/10.3852/14-175
Donoso Zegers, C. (1993). Estructura, variación y dinámica de bosques templados de Chile y Argentina. Ecología Forestal. Editorial Universitaria, Santiago, Chile.
Douanla-Meli, C. (2007). Fungi of Cameroon. Ecological diversity with emphasis on the taxonomy of Non-gilled Hymenomycetes from the Mbalmayo forest reserve. En Bibliotheca Mycologica (Vol. 202).
Doyle, J. J. y Doyle, J. L. (1990). Isolation of plant DNA from fresh tissue. Focus 12: 13-15.
Dumolin, S., Demesure, B. y Petit, R. J. (1995). Inheritance of chloroplast and mitochondrial genomes in pedunculate oak investigated with an efficient PCR method. Theoretical and Applied Genetics 91 (8): 1253-1256. https://doi.org/10.1007/BF00220937
Edgar, R. C. (2010). Search and clustering orders of magnitude faster than BLAST. Bioinformatics 26 (19): 2460-2461. https://doi.org/10.1093/bioinformatics/btq461
Edgar, R. C. (2016). SINTAX: a simple non-Bayesian taxonomy classifier for 16S and ITS sequences. bioRxiv 074161. https://doi.org/10.1101/074161
Edgar, R. C. y Flyvbjerg, H. (2015). Error filtering, pair assembly and error correction for next-generation sequencing reads. Bioinformatics 31 (21): 3476-3482. https://doi.org/10.1093/bioinformatics/btv401
Frøslev, T. G., Kjøller, R., Bruun, H. H., Ejrnæs, R., Brunbjerg, A. K., Pietroni, C. y Hansen, A. J. (2017). Algorithm for post-clustering curation of DNA amplicon data yields reliable biodiversity estimates. Nature Communications 8 (1): 1188. https://doi.org/10.1038/s41467-017-01312-x
Gardes, M. y Bruns, T. D. (1993). ITS primers with enhanced specificity for basidiomycetes - application to the identification of mycorrhizae and rusts. Molecular Ecology 2 (2): 113-118. https://doi.org/10.1111/j.1365-294X.1993.tb00005.x
Grossart, H.-P., Wurzbacher, C., James, T. Y. y Kagami, M. (2016). Discovery of dark matter fungi in aquatic ecosystems demands a reappraisal of the phylogeny and ecology of zoosporic fungi. Fungal Ecology 19: 28-38. https://doi.org/10.1016/j.funeco.2015.06.004
Hatakka, A. (2005). Biodegradation of lignin . En S. Alexander (ed.), Biopolymers Online. Wiley-VCH Verlag GmbH & Co. https://doi.org/10.1002/3527600035.bpol1005
Harrison, J. G. y Griffin, E. A. (2020). The diversity and distribution of endophytes across biomes, plant phylogeny and host tissues: how far have we come and where do we go from here? Environmental Microbiology 22 (6): 2107-2123. https://doi.org/10.1111/1462-2920.14968
Hibbett, D., Abarenkov, K., Kõljalg, U., Öpik, M., Chai, B., Cole, J., Wang, Q., Crous, P., Robert, V., Helgason, T., Herr, J. R., Kirk, P., Lueschow, S., O’Donnell, K., Nilsson, R. H., Oono, R., Schoch, C., Smyth, C., Walker, D. M., … Geiser, D. M. (2016). Sequence-based classification and identification of Fungi. Mycologia 108 (6): 1049-1068. https://doi.org/https://doi.org/10.3852/16-130
Hood, I. A., McDougal, R. L., Somchit, C., Kimberley, M. O., Lewis, A. S. R. y Hood, J. O. L. (2019). Fungi decaying the wood of fallen beech ( Nothofagus ) trees in the South Island of New Zealand. Canadian Journal of Forest Research 49 (1): 1-17. https://doi.org/10.1139/cjfr-2018-0179
Johnston, P. R., Johansen, R. B., Williams, A. F. R., Paula Wikie, J. y Park, D. (2012). Patterns of fungal diversity in New Zealand Nothofagus forests. Fungal Biology 116 (3): 401-412. https://doi.org/10.1016/j.funbio.2011.12.010
Johnston, P. R., Park, D. y Smissen, R. D. (2017). Comparing diversity of fungi from living leaves using culturing and high-throughput environmental sequencing. Mycologia 109 (4): 1-12. https://doi.org/10.1080/00275514.2017.1384712
Küngas, K., Bahram, M. y Põldmaa, K. (2020). Host tree organ is the primary driver of endophytic fungal community structure in a hemiboreal forest. FEMS Microbiology Ecology 96 (2): 1-10. https://doi.org/10.1093/femsec/fiz199
Kunkel, V., Wells, T. y Hancock, G. R. (2016). Soil temperature dynamics at the catchment scale. Geoderma 273: 32-44. https://doi.org/10.1016/j.geoderma.2016.03.011
McMurdie, P. J. y Holmes, S. (2013). phyloseq: An R Package for Reproducible Interactive Analysis and Graphics of Microbiome Census Data. PLoS ONE 8 (4): e61217. https://doi.org/10.1371/journal.pone.0061217
McMurdie, P. J. y Paulson, J. N. (2016). biomformat: An interface package for the BIOM file format. En R/Bioconductor Package.
Molina, L. (2022). Sanidad de los bosques de Nothofagus. Caracterización de sitio y organismos asociados a la muerte agrupada. Universidad de Buenos Aires.
Molina, L., Rajchenberg, M., de Errasti, A., Aime, M. C. y Pildain, M. B. (2020). Sapwood-inhabiting mycobiota and Nothofagus tree mortality in Patagonia: Diversity patterns according to tree species, plant compartment and health condition. Forest Ecology and Management 462: 117997. https://doi.org/10.1016/j.foreco.2020.117997
Nilsson, R. H., Anslan, S., Bahram, M., Wurzbacher, C., Baldrian, P. y Tedersoo, L. (2019). Mycobiome diversity: high-throughput sequencing and identification of fungi. Nature Reviews Microbiology 17 (2): 95-109. https://doi.org/10.1038/s41579-018-0116-y
Oksanen, J., Blanchet, F. G., Friendly, M., Kindt, R., Legendre, P., McGlinn, D., Minchin, P. R., O’Hara, R. B., Simpson, G. L., Solymos, P., Stevens, M. H. H., Szoecs, E. y Wagner, H. (2020). vegan: Community Ecology Package (2.5.7). https://cran.r-project.org/package=vegan
Palmer, J. M., Jusino, M. A., Banik, M. T. y Lindner, D. L. (2018). Non-biological synthetic spike-in controls and the AMPtk software pipeline improve mycobiome data. PeerJ 6 (5): e4925. https://doi.org/10.7717/peerj.4925
Pearson, K. (1900). X. On the criterion that a given system of deviations from the probable in the case of a correlated system of variables is such that it can be reasonably supposed to have arisen from random sampling. The London, Edinburgh, and Dublin Philosophical Magazine and Journal of Science 50 (302): 157-175. https://doi.org/10.1080/14786440009463897
Pildain, M. B., Coetzee, M. P. A., Rajchenberg, M., Petersen, R. H., Wingfield, M. J. y Wingfield, B. D. (2009). Molecular phylogeny of Armillaria from the Patagonian Andes. Mycological Progress 8 (3): 181-194. https://doi.org/10.1007/s11557-009-0590-8
Rajchenberg, M. (2006). Los políporos (Basidiomycetes) de los bosques Andino Patagónicos de Argentina. Schweizerbart’sche Verlagsbuchhandlung.
Raup, D. M. y Crick, R. E. (1979). Measurement of faunal similarity in paleontology. Journal of Paleontology 53 (5): 1213-1227. https://doi.org/https://www.jstor.org/stable/1304099
Riley, R., Salamov, A.A., Brown, D.W., Nagy, L.G., Floudas, D., Held, B.W. y Grigoriev, I.V. (2014). Extensive sampling of basidiomycete genomes demonstrates inadequacy of the white-rot/brown-rot paradigm for wood decay fungi. Proceedings of the National Academy of Sciences 111 (27). https://doi.org/10.1073/pnas.1400592111
Rim, S. O., Roy, M., Jeon, J., Montecillo, J. A. V., Park, S.-C. y Bae, H. (2021). Diversity and Communities of Fungal Endophytes from Four Pinus Species in Korea. Forests 12 (3): 302. https://doi.org/10.3390/f12030302
Robinson, R. M., Morrison, D. J. y Jensen, G. D. (2004). Necrophylactic periderm formation in the roots of western larch and Douglas-fir trees infected with Armillaria ostoyae. II. The response to the pathogen. Forest Pathology 34 (2): 119-129. https://doi.org/10.1111/j.1439-0329.2004.00354.x
Ryvarden, L. y Johansen, I. (1980). A preliminary polypore flora of East Africa. En A preliminary Polypore flora of East Africa. Fungiflora.
Tuor, U., Winterhalter, K. y Fiechter, A. (1995). Enzymes of white-rot fungi involved in lignin degradation and ecological determinants for wood decay. Journal of Biotechnology 41 (1): 1-17. https://doi.org/10.1016/0168-1656(95)00042-O
U’Ren, J. M., Lutzoni, F., Miadlikowska, J., Zimmerman, N. B., Carbone, I., May, G. y Arnold, A. E. (2019). Host availability drives distributions of fungal endophytes in the imperilled boreal realm. Nature Ecology & Evolution 3 (10): 1430-1437. https://doi.org/10.1038/s41559-019-0975-2
Vo?íšková, J., Brabcová, V., Cajthaml, T. y Baldrian, P. (2014). Seasonal dynamics of fungal communities in a temperate oak forest soil. New Phytologist 201 (1): 269-278. https://doi.org/10.1111/nph.12481
Wang, H. H., Chu, H. L., Dou, Q., Feng, H., Tang, M., Zhang, S. X. y Wang, C. Y. (2021). Seasonal Changes in Pinus tabuliformis Root-Associated Fungal Microbiota Drive N and P Cycling in Terrestrial Ecosystem. Frontiers in Microbiology 11: 526898. https://doi.org/10.3389/fmicb.2020.526898
White, T. J., Bruns, T., Lee, S. y Taylor, J. (1990). Amplification and direct sequencing of fungal ribosomal RNA genes for phylogenetics. En T. J. White, T. Bruns, S. J. W. T. Lee, J. Taylor, M. A. Innis, D. H. Gelfand, y J. J. Sninsky (Eds.), PCR protocols: a guide to methods and applications (pp. 315–322). Academic Press.
Wickham, H. (2016). ggplot2: Elegant Graphics for Data Analysis (3.3.3; Vol. 2, Número 1, pp. 1–189). Springer-Verlag. https://ggplot2.tidyverse.org
Descargas
Publicado
Cómo citar
Número
Sección
Licencia
Derechos de autor 2022 Lilloa

Esta obra está bajo una licencia internacional Creative Commons Atribución-NoComercial-SinDerivadas 4.0.